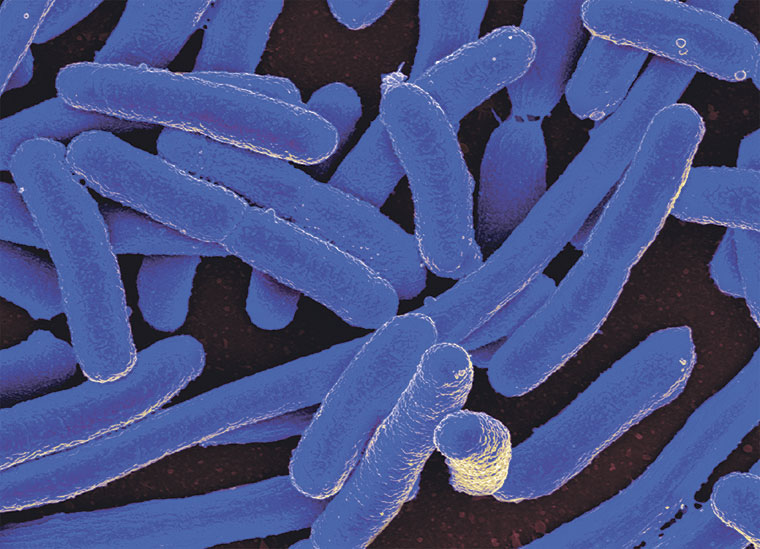
En esta ocasión no tendremos biografía al uso de una persona importante en la ciencia, bien por sus descubrimientos, bien por sus aportaciones al progreso social o cultural. Hoy traemos al que, probablemente, sea el ser vivo más conocido y estudiado del mundo, protagonista de la venganza de Moctezuma, la reina de las bacterias, el perejil de todas las salsas investigadoras y el primer nombre en latín que se aprende en las facultades de biología: su majestad, Escherichia coli (E. coli, para las amigas)
Nuestra protagonista es una enterobacteria y, concretamente, la bacteria anaerobia facultativa comensal más abundante de la microbiota del tracto gastrointestinal de los animales homeotermos (eso que antes se decía que eran de sangre caliente y el grupo al que pertenece nuestra especie), donde junto al resto de microorganismos que nos colonizan garantizan el proceso digestivo y la producción de vitaminas K y B. ¿Os sonaban solo cosas malas asociadas a nuestra bacteria? Pues sí. Aunque la mayoría de E. coli no genera ningún problema, también tiene una cara poco amable vinculada a diarreas, incluso hemorrágicas, insuficiencia renal y otras afecciones con consecuencia incluso de muerte. Poca broma con E. coli.
Por cierto, y hablando de diarreas, fue así como un joven pediatra la descubrió. Theodor Escherich, a finales del siglo XIX, mostraba un interés verdaderamente científico en las heces y, en concreto, en las heces de bebés. En 1885 publica un importante estudio, resultado de años de poner bajo el microscopio cacas infantiles con el fin de descubrir los microbios del intestino infantil y su papel tanto en la salud como en la enfermedad.
El Sr. Escherich no le puso su nombre a nuestra protagonista, sino que la nombró Bacterium coli commune. Y, aunque después fue descrita otras muchas veces con otros tantos nombres, finalmente en 1954 se establece el nombre de Escherichia coli como definitivo y en honor al primero en haberla descrito.
Es, como decíamos al principio, probablemente el organismo más estudiado; su genoma fue secuenciado en 1997 y se utilizó, mucho más adelante, un sistema de investigación abierta donde investigadores de distintas partes del mundo pudieron descifrar en tiempo récord los intríngulis de algo que traía de cabeza a Alemania: un brote de E. coli enterohemorrágica (EHEC). Internet, las redes sociales y el software libre permitieron un trabajo colaborativo que permitió, también, hacer la primera anotación funcional de nuestra bacteria. Y los avances que permiten la colaboración científica frente a la competencia son, como se demostró aquí, increíbles.
Pero, se pueden estar preguntando, además por su papel en el proceso digestivo o en la producción de determinadas vitaminas, ¿por qué es tan importante frente a otras bacterias que también tienen un papel clave en nuestro correcto funcionamiento?
En primer lugar, porque aunque su entrada en laboratorio fue a finales del siglo XIX, fue sobre todo a mediados del siguiente siglo cuando entró con fuerza como modelo para estudiar algunos de los fundamentos clave de la biología. Su sencillez y su facilidad para crecer y multiplicarse en distintos medios la llevaron a lo más alto de la investigación y ya pueden agradecerle varios Premio Nobel.
Concretamente 12 premios Nobel y la gloria de estar en el meollo del descubrimiento de una técnica revolucionaria: “cortar y pegar” el ADN para poder seleccionar secuencias concretas y darle un buen empujón a la ingeniería genética.
También permitió conocer la replicación del ADN y el papel del ARNm (mención de honor aquí a Severo Ochoa, que consiguió el Nobel gracias a sus estudios en ARN polimerasa) o cómo se regula la actividad de los genes en las bacterias.
¿Más? Ayudó a conocer mucho más sobre el papel de las mutaciones y, con su protagonismo ayudando a conseguir el primer organismo modificado genéticamente, ser protagonista en el ámbito de la biotecnología.
En los inicios de la investigación alrededor de esta bacteria, el interés radicaba especialmente en las infecciones que causaba y no tanto como modelo biológico. Pues bien, de alguna manera volvemos a los orígenes para enfrentar uno de los mayores problemas de salud pública al que hemos de dar respuesta actualmente: las resistencias a antibióticos, causa en países desarrollados de más del 50% de las enfermedades nosocomiales (las que se cogen en ámbitos hospitalarios).
Supongo que no requiere mucha explicación la importancia de combatir las resistencias a antibióticos que tantas vidas salvaron en el siglo XX y la necesidad de diseñar nuevos fármacos para las enfermedades emergentes.
En E.coli también encontramos casos de resistencias a antibióticos con consecuencias muy graves cuando hablamos de cepas que se encuentran fuera del intestino y están relacionadas con distintas infecciones urinarias, meningitis neonatal o septicemia.
¿En qué consisten estas resistencias? En que las bacterias, bien porque adquieran genes de otras bacterias bien porque se modifiquen los suyos, puedan inactivar o degradar el antibiótico. Y ante esto es clave conocer cómo ocurre esto, qué mecanismos hay detrás de la división de la célula para incidir en ese momento, evitando su reproducción, y diseñar nuevos medicamentos que consigan sortear las resistencias.
Una ciencia colaborativa, pública, abierta y que responda a la búsqueda de beneficios sociales y no económicos es fundamental en muchos ámbitos de la vida. En el ámbito sanitario, más aún.
Pero la ciencia la hacen personas, que deben tener situaciones laborales que les permitan desarrollar sus investigaciones dignamente con recursos suficientes.
Y, muchas veces, también organismos invisibles que se convierten en imprescindibles.